Una nueva arma para el diagnóstico de la tuberculosis y la detección de la resistencia a los fármacos: una secuenciación dirigida de nueva generación (tNGS) combinada con aprendizaje automático para el diagnóstico de la hipersensibilidad a la tuberculosis.
Informe bibliográfico: CCa: un modelo de diagnóstico basado en tNGS y aprendizaje automático, adecuado para personas con tuberculosis bacteriana leve y meningitis tuberculosa.
Título de la tesis: Secuenciación de próxima generación y aprendizaje automático dirigidos a la tuberculosis: una estrategia de diagnóstico ultrasensible para la presencia de pequeños túbulos pulmonares y meningitis tubular.
Periódico: 《Clínica Chimica Acta》
FI: 6.5
Fecha de publicación: enero de 2024

En colaboración con la Universidad de la Academia China de Ciencias y el Hospital Torácico de Beijing de la Universidad Médica Capital, Macro & Micro-Test desarrolló un modelo de diagnóstico de tuberculosis basado en la tecnología de secuenciación dirigida de nueva generación (tNGS) y el aprendizaje automático. Este modelo ofrece una sensibilidad de detección ultra alta para la tuberculosis con pocas bacterias y la meningitis tuberculosa, proporciona un nuevo método de diagnóstico de hipersensibilidad para el diagnóstico clínico de ambos tipos de tuberculosis y contribuye al diagnóstico preciso, la detección de la resistencia a los fármacos y el tratamiento de la tuberculosis. Asimismo, se ha descubierto que el ADN libre circulante (cfDNA) del plasma del paciente puede utilizarse como una muestra adecuada para la toma de muestras clínicas en el diagnóstico de la meningitis tuberculosa.
En este estudio, se utilizaron 227 muestras de plasma y líquido cefalorraquídeo para establecer dos cohortes clínicas. Las muestras de la cohorte de diagnóstico de laboratorio se utilizaron para establecer el modelo de aprendizaje automático para el diagnóstico de tuberculosis, y las muestras de la cohorte de diagnóstico clínico se utilizaron para verificar dicho modelo. Todas las muestras se analizaron inicialmente con una sonda de captura dirigida especialmente diseñada para Mycobacterium tuberculosis. Posteriormente, basándose en los datos de secuenciación TB-tNGS, se utilizó un modelo de árbol de decisión para realizar una validación cruzada de 5 pliegues en los conjuntos de entrenamiento y validación de la cola de diagnóstico de laboratorio, obteniéndose así los umbrales de diagnóstico para las muestras de plasma y líquido cefalorraquídeo. El umbral obtenido se introdujo en dos conjuntos de prueba de la cola de diagnóstico clínico para su detección, y el rendimiento diagnóstico del modelo se evaluó mediante la curva ROC. Finalmente, se obtuvo el modelo de diagnóstico de tuberculosis.
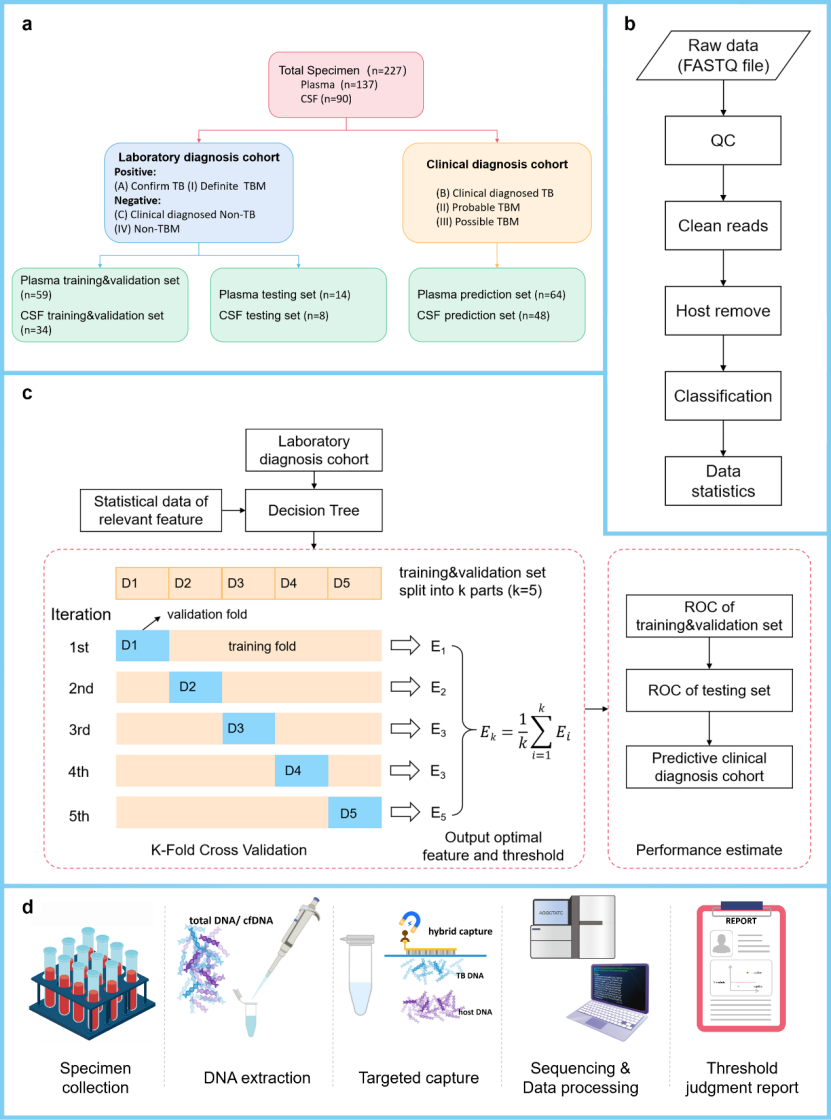
Figura 1. Diagrama esquemático del diseño de la investigación.
Resultados: Según los umbrales específicos de la muestra de ADN del LCR (AUC = 0,974) y la muestra de ADNcf del plasma (AUC = 0,908) determinados en este estudio, entre 227 muestras, la sensibilidad de la muestra de LCR fue del 97,01%, la especificidad del 95,65%, y la sensibilidad y especificidad de la muestra de plasma fueron del 82,61% y del 86,36%. En el análisis de 44 muestras pareadas de ADNcf del plasma y ADN del líquido cefalorraquídeo de pacientes con TBM, la estrategia diagnóstica de este estudio tiene una alta consistencia del 90,91% (40/44) en el ADNcf del plasma y el ADN del líquido cefalorraquídeo, y la sensibilidad es del 95,45% (42/44). En niños con tuberculosis pulmonar, la estrategia diagnóstica de este estudio es más sensible a las muestras de plasma que los resultados de detección Xpert de muestras de jugo gástrico de los mismos pacientes (28,57% frente a 15,38%).
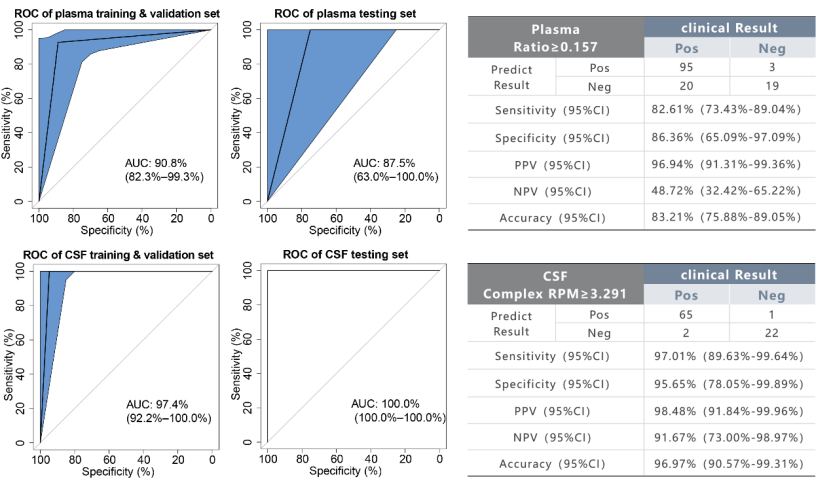
Figura 2. Rendimiento del análisis del modelo de diagnóstico de tuberculosis para muestras de población.
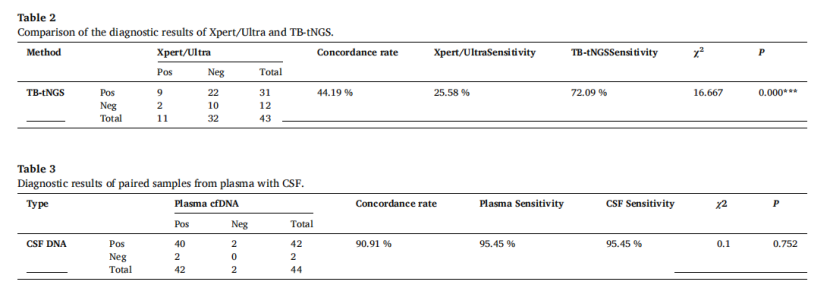
Figura 3. Resultados diagnósticos de muestras pareadas.
Conclusión: En este estudio se estableció un método de diagnóstico hipersensible para la tuberculosis, que puede proporcionar una herramienta diagnóstica con la mayor sensibilidad de detección para pacientes con tuberculosis oligobacilar (cultivo negativo). La detección de tuberculosis hipersensible basada en el ADN libre circulante en plasma puede ser un tipo de muestra adecuado para el diagnóstico de tuberculosis activa y meningitis tuberculosa (las muestras de plasma son más fáciles de obtener que el líquido cefalorraquídeo en pacientes con sospecha de tuberculosis cerebral).
Enlace original: https://www.sciencedirect.com/science/article/pii/s0009898123004990? via%3Dihub
Breve introducción a los productos de detección de tuberculosis de la serie Macro & Micro-Test.
Dada la complejidad de las muestras de pacientes con tuberculosis y sus diversas necesidades, Macro & Micro-Test ofrece un conjunto completo de soluciones NGS para la extracción por licuefacción de muestras de esputo, la construcción de bibliotecas Qualcomm, la secuenciación y el análisis de datos. Los productos abarcan el diagnóstico rápido de pacientes con tuberculosis, la detección de la resistencia a los fármacos, la tipificación de Mycobacterium tuberculosis y NTM, el diagnóstico de hipersensibilidad en tuberculosis con resultados negativos para bacterias y en personas con tuberculosis, entre otros.
Kits de detección seriada para tuberculosis y micobacterias:
| Número de artículo | nombre del producto | Contenido de las pruebas de productos | tipo de muestra | modelo aplicable |
| HWTS-3012 | Agente de liberación de muestra | Utilizado en el tratamiento de licuefacción de muestras de esputo, ha obtenido el número de registro de primera clase Sutong Machinery Equipment 20230047. | esputo | |
| HWTS-NGS-P00021 | Kit de detección cuantitativa Qualcomm para tuberculosis hipersensible (método de captura de sonda) | Detección no invasiva (biopsia líquida) de hipersensibilidad para tuberculosis pulmonar y nódulos cerebrales sin presencia de bacterias; las muestras de personas sospechosas de estar infectadas con tuberculosis o micobacterias no tuberculosas se analizaron mediante metagenómica de secuenciación de alta profundidad, y se proporcionó información sobre la detección de la infección por tuberculosis o micobacterias no tuberculosas, así como la información principal sobre la resistencia a los fármacos de primera línea de Mycobacterium tuberculosis. | Sangre periférica, líquido de lavado alveolar, hidrotórax y ascitis, muestra de punción focal, líquido cefalorraquídeo. | Segunda generación |
| HWTS-NGS-T001 | Kit de tipificación de micobacterias y detección de resistencia a fármacos (método de secuenciación por amplificación multiplex) | Prueba de tipificación de micobacterias, incluyendo MTBC y 187 NTM.;La detección de la resistencia a los fármacos de Mycobacterium tuberculosis abarca 13 fármacos y 16 sitios de mutación clave de los genes de resistencia a los fármacos. | Esputo, líquido de lavado alveolar, hidrotórax y ascitis, muestra de punción focal, líquido cefalorraquídeo. | Plataforma dual de segunda/tercera generación |
Aspectos destacados: Kit HWTS-NGS-T001 para la tipificación de micobacterias y la detección de resistencia a fármacos (método de amplificación multiplex).
Introducción del producto
El producto se basa en los principales fármacos de primera y segunda línea descritos en las directrices de la OMS para el tratamiento de la tuberculosis, los macrólidos y aminoglucósidos que se utilizan habitualmente en las directrices para el tratamiento de las micobacterias no tuberculosas (MNT), y los sitios de resistencia a los fármacos abarcan todo un grupo de sitios relacionados con la resistencia a los fármacos en el catálogo de mutaciones del complejo Mycobacterium tuberculosis de la OMS, así como otros genes de resistencia a los fármacos y sitios de mutación notificados según la investigación y las estadísticas de la literatura de alta puntuación a nivel nacional e internacional.
La identificación de la tipificación se basa en las cepas de NTM resumidas en las directrices sobre NTM publicadas por la Revista China de Tuberculosis y Enfermedades Respiratorias, así como en el consenso de expertos. Los cebadores de tipificación diseñados permiten amplificar, secuenciar y anotar más de 190 especies de NTM.
Mediante la tecnología de amplificación por PCR múltiple dirigida, se amplificaron los genes de genotipado y los genes de resistencia a fármacos de Mycobacterium, obteniéndose la combinación de amplicones de los genes diana a detectar. Los productos amplificados se pueden integrar en bibliotecas de secuenciación de alto rendimiento de segunda o tercera generación, y todas las plataformas de secuenciación de segunda y tercera generación pueden someterse a secuenciación de alta profundidad para obtener la información de secuencia de los genes diana. Al comparar con las mutaciones conocidas contenidas en la base de datos de referencia integrada (incluido el catálogo de mutaciones del complejo Mycobacterium tuberculosis de la OMS y su relación con la resistencia a fármacos), se determinaron las mutaciones relacionadas con la resistencia o susceptibilidad a los fármacos antituberculosos. En combinación con la solución de tratamiento de muestras de esputo de apertura automática de Macro & Micro-Test, se resolvió el problema de la baja eficiencia de amplificación de ácidos nucleicos de las muestras de esputo clínico (diez veces superior a la de los métodos tradicionales), de modo que la detección de la resistencia a fármacos mediante secuenciación se puede aplicar directamente a muestras de esputo clínico.
Rango de detección del producto
34genes relacionados con la resistencia a los fármacos18medicamentos antituberculosos y6Se detectaron fármacos NTM, que abarcan297Sitios de resistencia a los medicamentos; Diez tipos de Mycobacterium tuberculosis y más190Se detectaron diferentes tipos de NTM.
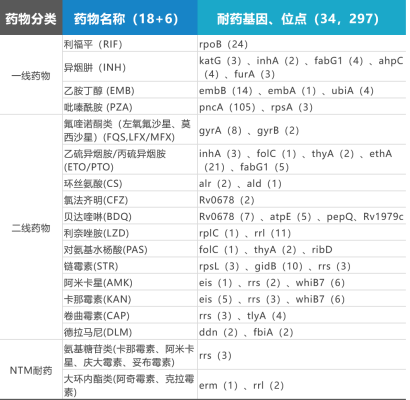
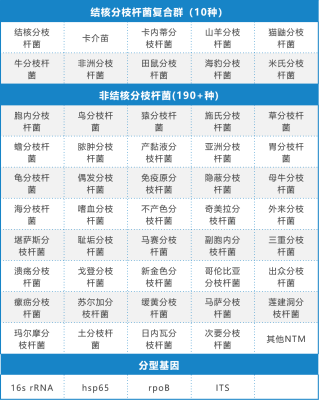
Tabla 1: Información de 18+6 fármacos +190+NTM
Ventaja del producto
Gran adaptabilidad clínica: las muestras de esputo pueden detectarse directamente con un agente de autolicuefacción sin necesidad de cultivo.
El proceso experimental es sencillo: la primera ronda de amplificación es simple y la construcción de la biblioteca se completa en 3 horas, lo que mejora la eficiencia del trabajo.
Tipificación integral y detección de resistencia a los fármacos: abarca la tipificación y los sitios de resistencia a los fármacos de MTB y NTM, que son los puntos clave de interés clínico, la tipificación precisa y la detección de resistencia a los fármacos, el soporte para software de análisis independiente y la generación de informes de análisis con un solo clic.
Compatibilidad: compatibilidad del producto, adaptándose a las plataformas ILM y MGI/ONT más comunes.
Especificaciones del producto
| Código de producto | nombre del producto | Plataforma de detección | presupuesto |
| HWTS-NGS-T001 | Kit de tipificación de micobacterias y detección de resistencia a fármacos (método de amplificación multiplex) | ONT、Illumina、MGI、Salus pro | 16/96rxn |
Fecha de publicación: 23 de enero de 2024
